实验 质粒DNA的碱裂解法提取与纯化
一、实验原理
细菌质粒是一类双链、闭环的DNA,大小范围从1kb至200kb以上不等。各种质粒都是存在于细胞质中、独立于细胞染色体之外的自主复制的遗传成份,通常情况下可持续稳定地处于染色体外的游离状态,但在一定条件下也会可逆地整合到寄主染色体上,随着染色体的复制而复制,并通过细胞分裂传递到后代。
质粒已成为目前最常用的基因克隆的载体分子,重要的条件是可获得大量纯化的质粒DNA分子。目前已有许多方法可用于质粒DNA的提取,本实验采用碱裂解法提取质粒DNA。
碱裂解法是一种应用最为广泛的制备质粒DNA的方法,其基本原理为:当菌体在NaOH和SDS溶液中裂解时,蛋白质与DNA发生变性,当加入中和液后,质粒DNA分子能够迅速复性,呈溶解状态,离心时留在上清中;蛋白质与染色体DNA不变性而呈絮状,离心时可沉淀下来。
纯化质粒DNA的方法通常是利用了质粒DNA相对较小及共价闭环两个性质。例如,氯化铯-溴化乙锭梯度平衡离心、离子交换层析、凝胶过滤层析、聚乙二醇分级沉淀等方法,但这些方法相对昂贵或费时。对于小量制备的质粒DNA,经过苯酚、氯仿抽提,RNA酶消化和乙醇沉淀等简单步骤去除残余蛋白质和RNA,所得纯化的质粒DNA已可满足细菌转化、DNA片段的分离和酶切、常规亚克隆及探针标记等要求,故在分子生物学实验室中常用。
二、实验试剂
1、溶液Ⅰ: 50mM葡萄糖,25mM Tris-HCl(pH 8.0),10mM EDTA(pH 8.0)。1M Tris-HCl(pH 8.0)12.5ml,0.5M EDTA(pH 8.0)10ml,葡萄糖4.730g,加ddH2O至500ml。在10 lbf/in2高压灭菌15min ,贮存于4℃。
2、溶液Ⅱ:0.2N NaOH,1% SDS。2N NaOH 1ml,10%SDS 1ml,加ddH2O至10ml。使用前临时配置。
3、溶液Ⅲ:醋酸钾(KAc)缓冲液,pH 4.8。5M KAc 300ml,冰醋酸 57.5ml,加ddH2O至500ml。4℃保存备用。
4、TE:10mM Tris-HCl(pH 8.0),1mM EDTA(pH 8.0)。1M Tris-HCl(pH 8.0)1ml,0.5M EDTA(pH 8.0)0.2ml,加ddH2O至100ml。15 lbf/in2高压湿热灭菌20min,4℃保存备用。
5、苯酚/氯仿/异戊醇(25:24:1)
6、乙醇(无水乙醇、70%乙醇)
7、5×TBE:Tris 碱54g,硼酸27.5g,EDTA-Na2·2H2O 4.65g,加ddH2O 至1000ml。15 lbf/in2高压湿热灭菌20min,4℃保存备用。
8、溴化乙锭(EB):10mg/ml
9、 RNase A(RNA酶A):不含DNA酶(DNase-free) RNase A的10mg/ml,TE配制,沸水加热15min,分装后贮存于-20℃。
10、6×loading buffer(上样缓冲液):0.25%溴酚蓝,0.25%二甲苯青FF,40%(W/V)蔗糖水溶液。
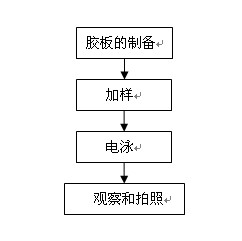
11、1% 琼脂糖凝胶:称取1g琼脂糖于三角烧瓶中,加100ml 0.5×TBE,微波炉加热至完全溶化,冷却至60℃左右,加EB母液(10mg/ml)至终浓度0.5μg/ml(注意:EB为强诱变剂,操作时带手套),轻轻摇匀。缓缓倒入架有梳子的电泳胶板中,勿使有气泡,静置冷却30min以上,轻轻拔出梳子,放入电泳槽中(电泳缓冲液0.5×TBE),即可上样。
三、实验操作
1、挑取LB固体培养基上生长的单菌落,接种于2.0ml LB(含相应抗生素)液体培养基中,37℃、250g振荡培养过夜(约12-14hr)。
2、取1.0ml培养物入微量离心管中,室温离心8000g×1min,弃上清,将离心管倒置,使液体尽可能流尽。
3、将细菌沉淀重悬于100μl预冷的溶液Ⅰ中,剧烈振荡,使菌体分散混匀。
4、加200μl新鲜配制的溶液Ⅱ,颠倒数次混匀(不要剧烈振荡),并将离心管放置于冰上2-3min,使细胞膜裂解(溶液Ⅱ为裂解液,故离心管中菌液逐渐变清)。
5、加入150μl预冷的溶液Ⅲ,将管温和颠倒数次混匀,见白色絮状沉淀,可在冰上放置3-5min。溶液Ⅲ为中和溶液,此时质粒DNA复性,染色体和蛋白质不可逆变性,形成不可溶复合物,同时K+使SDS-蛋白复合物沉淀,4℃离心8000g × 10min, 小心移出上清于一新微量离心管中。
6、加入450μl的苯酚/氯仿/异戊醇,振荡混匀,4℃离心8000g × 10min。
7、小心移出上清于一新微量离心管中,加入2.0倍体积(1ml)预冷的无水乙醇,混匀,室温放置5min,4℃离心12000g×10min,弃上清。
8、加入1ml预冷的70%乙醇洗涤沉淀1次,4℃离心8000g×7min,弃上清,将沉淀在室温下晾干或吹干(不能过于干燥,造成溶解困难)。
9、沉淀溶于20μl TE(含RNase A 20μg/ml),-20℃保存备用。
四、质粒DNA的电泳检测
观察琼脂凝胶中DNA的最简单方法是利用荧光染料溴化乙锭进行染色。该物质含有一个可以嵌入DNA的堆积碱基之间的一个平面基团,这个基团的固定位置及其与碱基的密切接近,导致染料与DNA结合并呈现荧光,其荧光产率比游离染料溶液有所增加。DNA吸收254nm处的紫外辐射并传递给染料,而被结合的染料本身则在302nm和366nm有光吸收。这两种情况下,被吸收的能量可在可见光谱红橙区的590nm处重新发射出来。因此,当凝胶中含有游离溴化乙锭时即可以检测到少量的DNA。
取制备的质粒DNA 1-2μl,加适当loading buffer混匀上样,采用 1-5V/cm的电压,使DNA分子从负极向正极移动至合适位置,取出凝胶置紫外灯下检测,摄片。
五、注意事项
本裂解法小量制备质粒 DNA重复性好,一般无麻烦。若所提取质粒 DNA不能被限制性内切酶切割,可通过酚/氯仿再次抽提,以清除杂质来解决问题。
六、习题:
1、什么是质粒?质粒有什么主要用途?
2、分子生物学实验中用的质粒是由野生型改建而来的,它必须具备哪三个基本要素?
3、制备的质粒DNA在琼脂糖凝胶上通常以三种形式条带存在,它们分别是什么?
实验 琼脂糖凝胶电泳实验
一、实验目的
(1) 学习琼脂糖凝胶电泳的基本原理;
(2) 掌握使用水平式电泳仪的方法;
二、实验原理
琼脂糖凝胶电泳是基因工程实验室中分离鉴定核酸的常规方法。核酸是两性电解质,其等电点为pH2-2.5,在常规的电泳缓冲液中(pH约8.5),核酸分子带负电荷,在电场中向正极移动。核酸分子在琼脂糖凝胶中泳动时,具有电荷效应和分子筛效应,但主要为分子筛效应。因此,核酸分子的迁移率由下列几种因素决定:
(1)DNA的分子大小。线状双链DNA分子在一定浓度琼脂糖凝胶中的迁移速率与DNA分子量对数成反比,分子越大则所受阻力越大,也越难于在凝胶孔隙中移动,因而迁移得越慢。
(2)DNA分子的构象。当DNA分子处于不同构象时,它在电场中移动距离不仅和分子量有关,还和它本身构象有关。相同分子量的线状、开环和超螺旋质粒DNA在琼脂糖凝胶中移动的速度是不一样的,超螺旋DNA移动得最快,而开环状DNA移动最慢。如在电泳鉴定质粒纯度时发现凝胶上有数条DNA带难以确定是质粒DNA不同构象引起还是因为含有其他DNA引起时,可从琼脂糖凝胶上将DNA带逐个回收,用同一种限制性内切酶分别水解,然后电泳,如在凝胶上出现相同的DNA图谱,则为同一种DNA。
(3)电源电压。在低电压时,线状DNA片段的迁移速率与所加电压成正比。但是随着电场强度的增加,不同分子量的DNA片段的迁移率将以不同的幅度增长,片段越大,因场强升高引起的迁移率升高幅度也越大,因此电压增加,琼脂糖凝胶的有效分离范围将缩小。要使大于2kb 的DNA 片段的分辨率达到最大,所加电压不得超过5v/cm。
(4)离子强度影响。电泳缓冲液的组成及其离子强度影响DNA的电泳迁移率。在没有离子存在时(如误用蒸馏水配制凝胶),电导率最小,DNA几乎不移动;在高离子强度的缓冲液中(如误加10×电泳缓冲液),则电导很高并明显产热,严重时会引起凝胶熔化或DNA变性。
溴化乙啶(Ethidium bromide, EB)(1) 能插入DNA分子中形成复合物,在波长为254nm紫外光照射下EB能发射荧光,而且荧光的强度正比于核酸的含量,如将已知浓度的标准样品作电泳对照,就可估算出待测样品的浓度。由于溴化乙啶有致癌的嫌疑, 所以现在也开发出了安全的染料,如Sybergreen。
常规的水平式琼脂糖凝胶电泳适合于DNA和RNA的分离鉴定;但经甲醛进行变性处理的琼脂糖电泳更适用于RNA的分离鉴定和Northern 杂交,因为变性后的RNA是单链,其泳动速度与相同大小的DNA分子量一样,因而可以进行RNA分子大小的测定,而且染色后条带更为锐利,也更牢固结合于硝酸纤维素膜上,与放射性或非放射性标记的探针发生高效杂交。
三、试剂与器材
(一)材料
电泳仪、水平电泳槽、样品梳子、琼脂糖等
(二)试剂
1、50*TAE(1000mL):242g Tris, 57.1mL 冰醋酸,18.6g EDTA。
2、EB溶液:100mL水中加入1g溴化乙啶,磁力搅拌数小时以确保其完全溶解,分装,室温避光保存。
3、DNA加样缓冲液:0.25%溴酚蓝,0.25%二甲苯青,50%甘油(w/v)。
4、DNA分子量标准
四、操作方法
常规的水平式琼脂糖电泳:
制备琼脂糖凝胶:按照被分离DNA分子的大小,决定凝胶中琼脂糖的百分含量;一般情况下,可参考下表:
琼脂糖的含量(%) 分离线状DNA分子的有效范围(Kb)
0.3 60-5
0.6 20-1
0.7 10-0.8
0.9 7-0.5
1.2 6-0.4
1.5 4-0.2
2.0 3-0.1
1、制备琼脂糖凝胶:称取琼脂糖,加入1x电泳缓冲液,待水合数分钟后,置微波炉中将琼脂糖融化均匀。在加热过程中要不时摇动,使附于瓶壁上的琼脂糖颗粒进入溶液;加热时应盖上封口膜,以减少水份蒸发。
2、胶板的制备:将胶槽置于制胶板上,插上样品梳子,注意观察梳子齿下缘应与胶槽底面保持1mm左右的间隙,待胶溶液冷却至50℃左右时,加入最终浓度为0.5微克/毫升的EB(也可不把EB加入凝胶中,而是电泳后再用0.5μg/ml的EB溶液浸泡染色15分钟),摇匀,轻轻倒入电泳制胶板上,除掉气泡;待凝胶冷却凝固后,垂直轻拔梳子;将凝胶放入电泳槽内,加入1x电泳缓冲液,使电泳缓冲液液面刚高出琼脂糖凝胶面;
3、加样:点样板或薄膜上混合DNA样品和上样缓冲液,上样缓冲液的最终稀释倍数应不小于1X。用10 μL微量移液器分别将样品加入胶板的样品小槽内,每加完一个样品,应更换一个加样头,以防污染,加样时勿碰坏样品孔周围的凝胶面。(注意:加样前要先记下加样的顺序和点样量)。
4、电泳:加样后的凝胶板立即通电进行电泳,DNA的迁移速度与电压成正比,最高电压不超过5V/cm。当琼脂糖浓度低于0.5%,电泳温度不能太高。样品由负极(黑色)向正极(红色)方向移动。电压升高,琼脂糖凝胶的有效分离范围降低。当溴酚蓝移动到距离胶板中央时,停止电泳。
5、观察和拍照:电泳完毕,取出凝胶。在波长为254nm的紫外灯下观察染色后(2)的或已加有EB的电泳胶板。DNA存在处显示出肉眼可辨的桔红色荧光条带。于凝胶成像系统中拍照并保存之。
五、注意事项
1、EB是强诱变剂并有中等毒性,易挥发,配制和使用时都应戴手套,并且不要把EB洒到桌面或地面上。凡是沾污了EB的容器或物品必须经专门处理后才能清洗或丢弃。简单处理方法为:加入大量的水进行稀释(达到0.5mg/mL以下),然后加入0.2倍体积新鲜配制的5%次磷酸(由50%次磷酸配制而成)和0.12倍体积新鲜配制的0.5mol/L 的亚硝酸钠,混匀,放置1天后,加入过量的1mol/L碳酸氢钠。如此处理后的EB的诱变活性可降至原来的1/200左右。
2、由于EB会嵌入到堆积的碱基对之间并拉长线状和带缺口的环状DNA,使DNA迁移率降低。因此,如果要准确地测定DNA的分子量,应该采用跑完电泳后再用0.5μg/ml的EB溶液浸泡染色的方法。
六、实验报告要求与思考题
1、附上电泳结果的图片并进行正确的标注(如下图)

M:1Kb DNA ladder;1:质粒DNA
2、琼脂糖凝胶电泳中DNA分子迁移率受哪些因素的影响?
3、如果样品电泳后很久都没有跑出点样孔,你认为有哪几方面的原因?
4、为什么分子生物学实施时要担心EB?
5、琼脂糖凝胶电泳时胶中DNA是靠什么发出荧光的?为什么?
电泳流程图:
实验 PCR扩增eGFP基因
一、PCR技术的基本原理
PCR类似于DNA的天然复制过程,其特异性依赖于与靶序列两端互补的寡核苷酸引物。PCR由变性--退火--延伸三个基本反应步骤构成:
①模板DNA的变性:模板DNA经加热至93℃左右一定时间后,使模板DNA双链或经PCR扩增形成的双链DNA解离,使之成为单链,以便它与引物结合,为下轮反应作准备;
②模板DNA与引物的退火(复性):模板DNA经加热变性成单链后,温度降至55℃左右,引物与模板DNA单链的互补序列配对结合;
③引物的延伸:DNA模板--引物结合物在TaqDNA聚合酶的作用下,以dNTP为反应原料,靶序列为模板,按碱基配对与半保留复制原理,合成一条新的与模板DNA 链互补的半保留复制链重复循环变性--退火--延伸三过程,就可获得更多的“半保留复制链”,而且这种新链又可成为下次循环的模板。每完成一个循环需2~4分钟, 2~3小时就能将待扩目的基因扩增放大几百万倍。(Plateau)。 到达平台期所需循环次数取决于样品中模板的拷贝。
PCR 技术应用广泛,不可能有这样一套条件满足所有的实验,但本实验所介绍的方法可适应于大多数DNA 扩增反应,即使有的不适应,至少也确定了一个共同的起点,在此基础上可以作多种变化。不过下列因素在实验应用时应予以特别注意,以求取得满意结果。
1、模板:单、双链DNA 和RNA都可以作为PCR样品,若起始材料是RNA,须先通过逆转录得取第一条cDNA。虽然PCR 可以仅用极微量的样品,但为了保证反应的特异性,一般宜用ng 量级的克隆DNA,ug 级的染色体DNA,待扩增样品质量要求较低,但不能混合有任何蛋白酶、核酸酶,Taq DNA聚合酶的抑制剂以及能结合DNA 的蛋白质。
2、引物:引物是决定PCR 结果的关键,下列原则有助于引物的合理设计。(1)尽可能选择碱基随机分布,GC 含量类似于被扩增片段的引物,尽量避免具有多聚嘌呤、多聚嘧啶或其它异常序列的引物。(2 )避免具有明显二级结构(尤其是在引物3'—末端)的序列。
3、防止引物间的互补,特别要注意避免具有3'末端重叠的序列。
4、引物的长度约为20个碱基,较长引物较好,但成本增加,短引物则特异性降低。
5、引物浓度不宜偏高,过高易形成二聚体解链;然后冷却至37—55℃,使引物与模板退
二、实验试剂
(一)仪器与器皿
PRC 扩增仪,琼脂糖凝胶电泳设备,微量取样器,一次性eppendorf管,凝胶成像仪
(二)试剂与材料
1、琼脂糖凝胶电泳试剂
1)电泳缓冲液:Tris—乙酸0.04mol/L PH8.0 0.002mol/L EDTA
2)加样缓冲液:0.25%溴酚兰40% w/v蔗糖
3)溴化乙锭溶液:0.05mg/ml溴化乙锭/水
4)琼脂糖
2、TaqDNA 多聚酶
3、5´反应缓冲液:
125mmol/L Tris-HCl pH8.2;10mmol/L MgCl2;0.5mg/ml gelatin;125mmol/L(NH4)2SO4; Formamide 25%
4、混合dNTP 液(dATP dGTP dTTP dCTP各2.5 mmol/L)
5、DNA 模板
6、引物 1 (10μmol/L)
7、引物 2 (10μmol/L)
8、无菌水
三、实验步骤
1、按顺序在200μl 指形管中加入以下试剂与样品:(因购入的试剂批次不同,加样时有所差别,以预实验结果为准。
1) ddH2O 37μl
2) 10*Buffer 5μl(含有MgCL2)
3) dNTP 2μl
4) 引物1(上游) 2μl
5) 引物2(下游)2μl
6) 模板 1μl (pEGFP质粒)
7) TaqDNA聚合酶1μl (2.5U)
总体积共50μl
2、在PCR 扩增仪上按以下反应条件编入程序:(以下为参考值,因扩增的DNA片段不同,各类PCR 扩增仪程序设定各不相同,编程过程视扩增的DNA 片段的要求及仪器而定参数。)
1) 预变性 94℃ 3 分种
2) 循环条件(30 次)
变性 94℃ 30 秒
复性 55℃ 30 秒
延伸 72℃ 1分
3) 延长延伸 72℃ 7 分钟
编完反应程序,置反应管于PCR扩增仪的反应孔中,开动机器,扩增循环反应开始。
3、 PCR 扩增完毕,配1.5%琼脂糖凝胶,电泳观察结果。
4、凝胶成像仪或紫外灯下观察实验结果,是否已扩增到实验设计的DNA片段
四、习题
1、PCR反应液中主要成分是哪些?在PCR反应过程中各起什么作用?
2、为什么在PCR反应过程中,使用三个不同的温度变化?
3、用PCR扩增目的基因,要想得到特异性产物需注意哪些事项?
实验 从动物组织(猪肝)中提取DNA
一、实验内容
采用SDS裂解和蛋白酶K消化法从猪肝中提取DNA,并进行琼脂糖凝胶电泳分析。
目的
(1) 掌握SDS裂解法从猪肝中的原理和方法;
(2) 巩固DNA的琼脂糖凝胶电泳分析实验。
二、实验原理
DNA是一切生物细胞的重要组成成分,主要存在于细胞核中。通过研磨和SDS作用破碎细胞;苯酚和氯仿可使蛋白质变性,用其混合液(酚:氯仿:异戊醇)重复抽提,使蛋白质变性,然后离心除去变性蛋白质;RNase降解RNA,从而得到纯净的DNA分子。
三、实验材料
新鲜猪肝
TES 缓冲液 : pH8.0 Tris-HCl 10 mmoL/L , EDTA 1mmoL/ L , SDS 0.1 mmoL/ L
四、实验步骤
1、剪取约0.5g肝脏组织,放入到研钵中磨碎;
2、向研钵中再加入1 ml TES轻轻研磨,将TES与破碎的组织混匀;
3、吸取535 µl组织匀浆液于2 ml EP管中,再加入60 µl SDS(10%),5.0 µl蛋白酶K,充分混匀后,于56°C保温1 h,每30分钟轻摇1次;
4、放置到室温,加入等体积饱和酚(600µl),颠倒混匀,11000 rpm,离心10 min,吸取400 µl水相,并转移至一个新的1.5 ml离心管中;
5、加入2倍体积(1000 µl)的无水乙醇和1/10倍体积(40 µl)3 M 醋酸钠沉淀DNA,12000 rpm离心10 min,弃乙醇;
6、加入适量TE溶解DNA和RNAse A(具体依DNA的多少而定),并利用0.7%的琼
脂溏进行电泳分析。
五、注意事项
1、在将猪肝剪碎前要将猪肝清洗干净,除去脂肪及系膜成分。
2、抽提每一步用力要柔和,防止机械剪切力对DNA的损伤。
3、取上层清液时,注意不要吸起中间的蛋白质层。
4、乙醇漂洗去乙醇时,不要荡起DNA。
5、离心后,不要晃动离心管,拿管要稳。
6、在乙醇沉淀后,经离心要观察留在EP管中的小白点,其主要成分就是DNA,在以后的实验中都要细心观察,防止因将小白点丢失。
六、习题
1、为了获得高质量的肝脏DNA,在实验过程中应注意什么。
2、结合本人操作体会,总结在提取过程中如何避免大分子DNA的降解。
3、核酸提取中,去除蛋白质的方法有哪些?
实验 限制性内切酶切割DNA
一、实验目的
1. 通过对DNA的酶切,学会设计构建体外重组DNA分子;
2. 根据目的基因合理选择载体与限制性内切酶;
3. 掌握DNA的酶切技术。
二、实验原理
限制性内切酶是从细菌中分离出来的一种能在特异位点切割DNA分子的核酸内切酶,目前已从多种细菌中分离出超过400种,识别各自不同的核苷酸顺序,这一顺序大多为具有一对称中心的回文序列,如从大肠杆菌中分离的 EcoR I识别…GAATTC… 切割后产生…CTTAAG… 、 …G 和 AATTC…的末端,
…CTTAAG…该末端由于有一段小的能互补配对的单链突出,故称为粘性末端。切割后的末端为3’-OH和5’-磷酸基团,即…G-OH和…CTTAA-P。
有的限制性酶识别四碱基对的顺序,如 San3A识别…GATC …;有的识别六
碱基对,如上述的ECOR I。识别四碱基对的内切酶由于识别顺序在DNA出现的频率更高(四碱基酶为44=256,六碱基酶为46=4096),因而可将DNA切割成更小的片段,而识别八碱基对的Not I…GCGGCCGC…、…CGCCGGCG… 则识别和切割位点更少(48=65536),但碱基并不以均等的概率出现,因而切割后产生的片段变化范围很大。
限制性内切酶作用的温度一般为37℃,反应体系中以Mg2+为唯一的辅助因子,且要求pH缓冲在7.5左右。
商品酶都保存在50%的甘油溶液中,-20℃贮存,活性通常较高,5u/μl(每单位即最适条件下1小时内完全酶解1μg DNA的酶量)。
三、实验材料
待酶切的DNA样品
四、实验仪器、器皿及试剂
1、仪器:可调微量加样器、恒温水浴箱、电泳仪、电泳槽、紫外检测灯
2、器皿:Eppendorf管、Tip、试管架
3、试剂:标准DNA (Marker)
EcoRI限制性内切酶
10×buffer:50mmol/l NaCl
10mmol/l Tris-HCl(pH7.5)
10mmol/l MgCl2
lmmol/l DTT(二硫苏糖醇)
五、实验步骤
1、将DNA样品8.5μl (质粒pEGFP, 1μg)
2、加入1μl 10×buffer,酶解buffer由厂家提供。
3、加入1u(0.5μl)的限制性内切酶EcoRI(限制性酶很昂贵,从-20℃取出要置于冰上,吸取要新的Tip头,以免污染杂质,吸完后尽快放回冰箱)。
4、混匀反应液后,稍离心使液体聚集,置37℃温育1小时。
5、进行电泳检查酶切结果,100V 25分钟。
6、紫外灯下观察消化效果。
六、注意事项
1、分子生物学实验大多为微量操作,DNA样品与限制性内切酶的用量都极少,必须严格注意吸样量的准确性以保证酶切效果最佳。现介绍三种微量取样方法:
(1)吸样时,将Tip尖刚刚接触到液面时,轻轻吸取。此法可吸取0.2~0.5μl的样品,注意不要将Tip尖全部插入溶液,这样Tip壁上会沾上很多的样品,导致吸样不准。
(2)用1cm长的塑料毛细管代替Tip吸样,此法也可吸取0.2~0.5μl的样量。
(3)目前也有细长Tip出售,专门用于吸取微量样品。
2、限制性内切酶价格比较贵,因此要注意不使其污染而导致浪费。这就要求每次吸酶时要用新的无菌Tip。另一个造成限制性内切酶浪费的因素就是限制性内切酶的失活。因此,要注意加样次序,即各项试剂加好后,最后才加酶,并要在冰上操作,且操作要尽可能快,以使限制性内切酶拿出冰箱的时间尽可能短。
若用同一酶消化很多样品时,可先计算出所需酶量(可稍多计一点),取出此量的酶与1×缓冲液混合,然后再分装至各个反应管内。这样可节约用酶且缩短操作过程、减少污染机会。
3、开启Eppendorf管时,手不要接触到管盖内面,以防杂酶污染。
4、样品在37℃与65℃保温时,要注意将Eppendorf管盖严,以防水进入管内造成实验失败。
5、无实验必要应尽量避免长时间酶消化样品。因长时间消化,限制酶溶液中可能存在的杂酶会影响试验结果。
七、习题
1、限制性核酸内切酶天然存在于什么生物体内?
2、什么是细菌的限制-修饰系统?限制-修饰系统对细菌有什么用途?
3、限制性内切酶有几类?这几类限制性内切酶各有什么特点?可作为工具酶的限制性内切酶是哪一类?为什么?
4、限制性内切酶的识别序列有什么特点?称为什么序列?
5、酶通常在什么温度中保存?为什么酶在该温度下保存不会结冻?酶最后工作的时候其甘油浓度必须低于多少?
6、1个单位(1 U)的限制性内切酶代表什么意思?
实验 质粒的转化
一、实验目的
掌握热激法或电转化法转化大肠杆菌感受态细胞及转化子的鉴定方法。
实验材料:质粒DNA;大肠杆菌感受态细胞。
二、实验原理
质粒的转化是指将质粒或以它为载体构建的重组子导入细菌的过程。将连接产物转化到感受态细胞中,实现重组克隆的增殖,便于后续分子操作。可以采用多种方法筛选和鉴定目的克隆。
(1)热激法:大肠杆菌在0℃ CaCl2低渗溶液中,菌细胞膨胀成球形,转化混合物中的DNA形成抗DNase的羟基-钙磷酸复合物粘附于细胞表面,经42℃短时间热冲击处理,促进细胞吸收DNA复合物,在丰富培养基上生长数小时后,球状细胞复原并分裂增殖。在被转化的细胞中,重组子基因得到表达,在选择性培养基平板上可挑选所需的转化子。
(2)电转化法:外加于细胞膜上的电场造成细胞膜的不稳定,形成电穿孔,不仅有利于离子和水进入细菌细胞,也有利于孔DNA等大分子进入。同时DNA在电场中形成的极性对于它运输进细胞也是非常重要的。
三、实验步骤
1、制备选择性培养基平板:在融化的250ml LB固体培养基中(冷却止55摄氏度以下)加入Amp至终浓度50μg/ml,混匀后倒入灭菌培养皿中;
2、取出1管制备好的感受态细胞,放在冰上融化;
3、每100μl感受态细胞加入约20ng质粒DNA,轻轻混匀,在冰上放置30分钟;
4、热击:将离心管放置42℃水浴,热击90秒,注意:勿摇动离心管;
5、冰镇:快速将离心管转移至冰浴,放置1-2分钟;
6、复苏:每管加400 μl LB培养基,在37℃摇床温和摇动温育45分钟,使细菌复苏;
7、布皿:取适当体积均匀涂布于含有、抗生素(Amp)的LB平板;
8、 培养:倒置培养皿,于37℃培养12-16小时即可观察到白色的菌落,即为转化子。
四、结果与分析
计算转化效率
菌落数/DNA质量(μg)*稀释倍数
五、习题
1、制备感受态细胞的关键是什么?
2、如果DNA转化后,没有得到转化子或者转化子很少,分析原因。
3、如何提高转化效率?
